Eseguirò analisi di single cell rna seq e annotazione del tipo cellulare
Sviluppatore di pipeline bioinformatiche
Informazioni su questo servizio
Hai dati di single-cell RNA-seq che necessitano di
analisi professionale e identificazione del tipo cellulare?
Analizzerò il tuo dataset scRNA-seq usando Seurat
e consegnerò un'annotazione completa del tipo cellulare con
visualizzazioni pronte per la pubblicazione.
COSA OTTIENI:
- Controllo qualità e filtraggio delle cellule di bassa qualità
- Normalizzazione e scaling
- Riduzione della dimensionalità con PCA
- Clustering basato su grafi
- Visualizzazione UMAP
- Identificazione di geni marcatori per cluster
- Annotazione biologica del tipo cellulare
- Relazione completa dell'analisi
LA MIA ESPERIENZA:
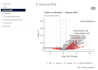
Ho analizzato 2.700 PBMC umani identificando 9 popolazioni cellulari diverse
tra cui T, B, NK, monociti, cellule dendritiche e piastrine usando Seurat.
Pipeline completa disponibile su GitHub.
COSA HO BISOGNO DA TE:
- File di output di 10X Genomics (barcodes, features, matrix)
O matrice di conteggio processata
- Nome dell'organismo (umano, topo, ecc.)
- Qualsiasi informazione biologica nota sul tuo campione
STRUMENTI: R, Seurat, ggplot2, dplyr, UMAP,
PCA, Git, Linux
Contattami prima di ordinare per discutere
il tuo dataset. Confermerò prima la fattibilità.
Expertise:
Classificazione
•
clustering
•
Analisi predittiva
Linguaggio di programmazione:
Python
•
R
Framework:
Panda
API:
Altro
Strumenti:
Quaderno jupyter
•
Colab